基于基因组序列数据的医学剂的创新筛选方法
由Leibniz Institute DSMZ-German的生物经济学和健康研究系主管Yvonne Mast教授领导的科学家团队,在下萨克森州Braunschweig的微生物和细胞培养物收集,已开发出一种新的筛查战略医疗物质。该策略仅基于分析基因组序列数据。
总结了她方法的优势,Mast解释说:“我们的预测策略的优势是,它可用于纯粹用于数字筛查,并且对于特定的潜在药物生产者而言非常有效,并且在某些情况下可以筛选出来细菌菌株最有可能产生已知物质。这使得分析和发现活性成分的过程变得更加容易。这个新方法是在发现新的活性成分的基因组开采研究领域的另一个重要贡献。”
近年来,已发现和开发较少的新活性成分(例如抗生素)用于医疗用途,同时在全球范围内迅速增加了多药病原体的威胁。医学药物研究中的一个主要问题是已经已知的物质的高回收率,这使得常规的筛查方法效率很低。
主动成分研究领域的数字化
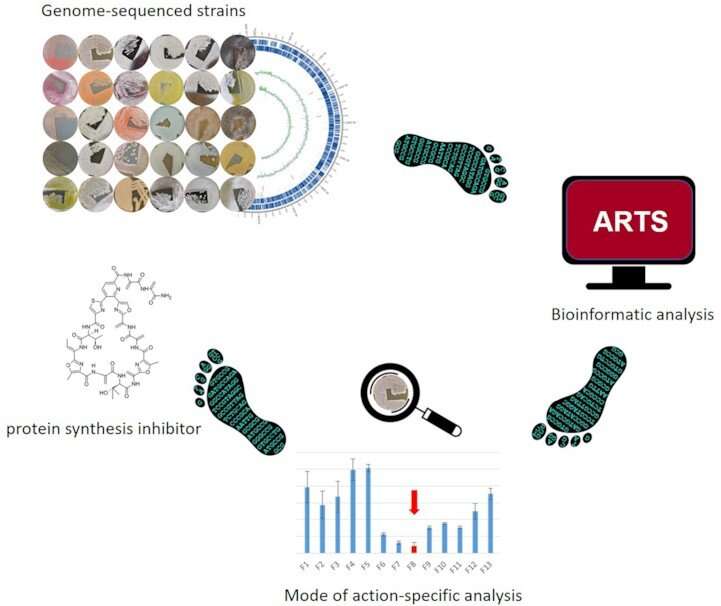
数字序列信息在主动成分研究中越来越重要。由微生物学家教授Yvonne Mast的团队基于细菌活性成分生产者的基因组序列信息制定了一种预测策略,这使得可以预测特定活性成分的产生,即所谓的蛋白质合成抑制剂。这些活性成分靶向细菌核糖体,这是许多重要的抗生素(如红霉素,四环素和克林霉素)的重要作用。
总部位于Braunschweig的科学家团队能够通过从细菌性放线菌的药物生产者基因组中识别特定指标基因来得出其预测策略,这表明蛋白质生物合成抑制剂合成性能。科学家通过鉴定来自DSMZ细菌收集的各种放线菌素菌株的蛋白质生物合成抑制剂氨基酸氨基菌素提供了功能证明。该方法已被命名为ψ-footprinting,最近发表在NAR基因组学和生物信息学。
进一步探索